
14/07/2020 - Nota de prensa
El resultado del estudio, que publica Nature Methods, puede facilitar el desarrollo de nuevos fármacos relacionados con enfermedades como el cáncer o el Alzheimerr
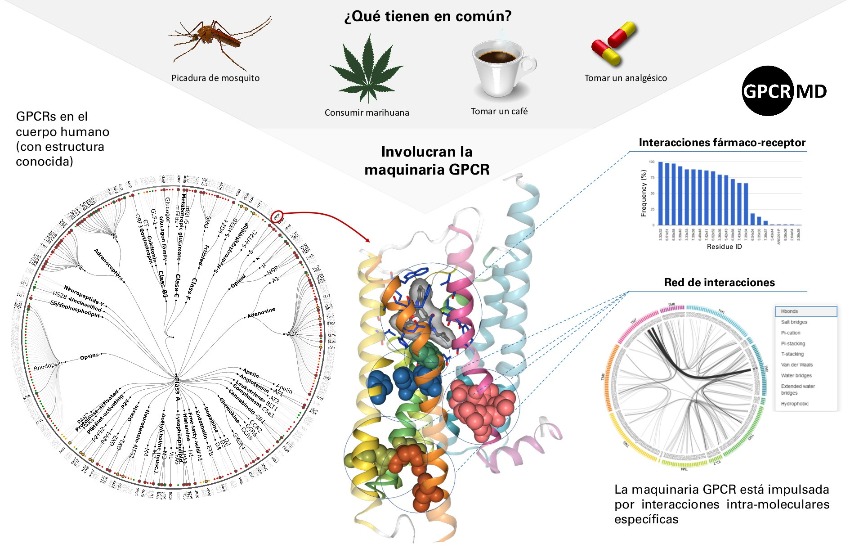
Los receptores acoplados a proteína G (GPCRs) son uno de los elementos básicos en la respuesta a estímulos como la picadura de un mosquito o la emoción que sentimos ante un gol de nuestro equipo de fútbol favorito. De hecho, son diana de casi el 40% de los fármacos actuales. Pero, hasta ahora, los investigadores no disponían de una herramienta que empleara simulaciones moleculares para analizar y entender completamente su función.
Es por ello que un consorcio formado por 23 instituciones de 10 países de Europa y de los Estados Unidos han aunado esfuerzos para diseñar una herramienta que permita comprender mejor el funcionamiento de estos receptores, cuyo trabajo consiste en transmitir señales al interior de la célula. La plataforma GPCRmd es el fruto de este trabajo, liderado y coordinado por el Grupo de investigación en desarrollo de fármacos en base a GPCRs del Programa de Investigación en Informática Biomédica (GRIB) del Instituto Hospital del Mar de Investigaciones Médicas (IMIM) y la Universitat Pompeu Fabra. En él también han participado de forma destacada investigadores del Instituto Paul Scherrer (PSI) de Suiza y de la Universitat Autònoma de Barcelona.
La Dra. Jana Selent, investigadora Miguel Servet en el IMIM y autora principal del estudio, explica que "hemos utilizado una tecnología de última generación, que requiere de un conocimiento muy específico, como son las simulaciones moleculares, para generar un recurso en línea en el cual los científicos de distintas disciplinas pueden, fácilmente, inspeccionar y analizar un exhaustivo número de simulaciones moleculares de GPCRs". Esto les permitirá, según el Dr. Ramon Guixà-González, investigador postdoctoral en el PSI de Suiza y coautor principal de este estudio, "extraer información relevante para el estudio y el desarrollo de nuevos fármacos relacionados con enfermedades tan importantes como el cáncer y el Alzheimer". Otros autores principales del estudio son Ismael Rodríguez Espigares y Mariona Torrens Fontanals, investigadores postdoctoral y predoctoral del GRIB.
Fuente: IMIM
Simulaciones a nivel atómico para entender cómo funcionan
Los GPCRs se encuentran en la membrana celular y transmiten la información que provoca las respuestas fisiológicas del cuerpo al interior de la célula. Por este motivo, son de vital importancia para muchos fármacos. La nueva plataforma permite analizar su funcionamiento a muy pequeña escala, a nivel atómico, con la ayuda de un nuevo software desarrollado recientemente. Gracias a él, las simulaciones realizadas, utilizando un protocolo común, por cada uno de los grupos que forman parte del consorcio, se han podido transferir y visualizar usando un simple navegador. Esto permite explotar la información en línea y de forma abierta para el uso de todos los investigadores trabajando en el desarrollo de nuevos tratamientos que tengan como diana los GPCRs.
En la actualidad, esta herramienta cubre aproximadamente el 70% de los GPCRs con estructura conocida. El objetivo de los investigadores es llegar al 100% y, a la vez, crear una herramienta que realice de forma automática la simulación y la publicación de nuevas simulaciones. No descartan que este sistema se pueda exportar en el futuro a otras familias de proteínas con interés para el desarrollo de nuevos fármacos.

Equipo investigador. Fuente: IMIM.
Artículo de referencia:
Rodriguez-Espigares et al. GPCRmd unveils the dynamics of the 3D-GPCRome. 2020, Nature Methods; https://www.nature.com/articles/s41592-020-0884-y
© Institut Hospital del Mar
d'Investigacions MèdiquesAviso legal y Política de Privacidad | Política de cookies | Mapa Web | Accesibilidad | Dirección y accesos | Contacto